
- •Редактирование Структуры
- •Выбор Силового поля
- •Оптимизация отдельной Молекулы
- •Сохранение Структуры
- •Упражнение 2: Сольватировать Структуру
- •Установка Периодических граничных условий
- •Определение Размера Periodic Box
- •Покажите Сольватированную Систему
- •Наладка Cutoffs и Dielectric Options
- •Оптимизация Сольватированной Молекулы
- •Упражнение 3: Использование Суперпозиции
- •Удаление Молекул воды
- •Соединение Двух Систем
- •Упражнение 4: Моделируемое нагревание
- •Установка Усреднение данных из Молекулярной Динамики
- •Продолжение Динамики
- •Реоптимизирование новой структуры
- •Часть 2: Моделирование Монте Карло
- •Установка усреднения из Монте Карло
- •Продолжение Моделирования и Анализа
Упражнение 4: Моделируемое нагревание
Здесь Вы используете молекулярную динамику, чтобы прогреть систему, чтобы получить более низкую энергию minimum. Вы должны сначала восстановить сольватированную систему цвиттериона аланина, чтобы выполнить с ним молекулярную динамику.
Восстановить сольватированную систему:
1. Открыть файл hin.
2. Если необходимо, пометить Show Periodic Box, чтобы показать периодический блок, который Вы определили ранее.
3. Если необходимо, удалите обозначения с экрана.
Устанавливать моделирование динамики:
1. Выбрать Molecular Dynamics на меню Compute.
Ячейка диалога Molecular Dynamics Options позволяет Вам устанавливать выбор для вычисления молекулярной динамики.
Движение динамики имеет три различных фазы: нагревание, движение, и охлаждение.
Первая фаза встречается в начальный период времени моделирования нагрева, используя температуру старта, для того чтобы увеличить начальные скорости до скоростей достигающих температуры моделирования.
В средней фазе, скорости повторно масштабируются только, если выбрана постоянная температура.
Заключительная
фаза проходит в период времени
моделирования охлаждения, с изменением
скоростей , чтобы достигнуть конечной
температуры.
2. Установить Heat time в 0.1 пикосекунд.
3. Установить Temperature step на 30К.
Потому что в начале старта градиент очень маленький (соответствующий, почти нулевой температуре), используется короткое время нагрева в 0.1 пикосекунд, чтобы поднять температуру от температуры старта 100 K до температуры моделирования в 300К с температурным шагом по 30К.
4. Установить Run time на 0.5 пикосекунд.
Температуры используются здесь, чтобы установить начальные скорости атома или регулировать скорости атома. Эта кинетическая энергия может быть преобразована в потенциальную энергию в течение моделирования, заставляя расчетную температуру понизиться. Если температура, в конечном счете, повышается (как делается в этом примере), это означает, что потенциальная энергия преобразовывается в кинетическую энергию, поскольку система перемещается в более устойчивую конформацию.
5. Удостоверитесь, что включен выбор Periodic boundary conditions. Этот выбор - автоматически отмечает HYPERCHEM, когда используются периодические граничные условия, но он может быть изменен выбирая опцию In vacuo.
6. Установить Step Size в 0.0005 пикосекунд.
7. Установить Data Collection period на 4. Для систем типа этой, которые имеют, видимые водородные атомы, размер шага в 0.5 fs точно соответствует объединению водорода, растягивающего движение. Вы можете модернизировать экран, используя любое число шагов времени, чтобы показать молекулярную динамику в реальном масштабе времени. В зависимости от прменяемых аппаратных средств ЭВМ которые Вы собираетесь использовать, данные могут слишком замедлять движение частиц, так что лучше установить Data collection period на 4.
8. Отменить Constant Temperature .
9.
Параметры настройки в ячейке диалога
должны напоминать вот это: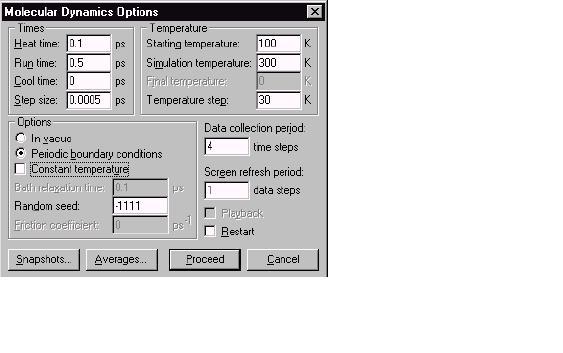
Установка Воспроизведения Динамики.
Молекулярная динамика моделирует развитие системы через какое-то время, при создании траектории атомных позиций и скоростей.
Устанавливать воспроизведение динамики:
1. Выбрать Snapshots внизу ячейки диалога Molecular Dynamics Options.
Открывается ячейка диалога Molecular Dynamics Snapshots.
2. Войти в имя файла ala-run. HYPERCHEM производит два файла с приставкой ala-run. Один файл, ala-run .hin, является HIN файлом, который содержит пуск картинки. Другой файл, ala-run .snp, является двоичным файлом, содержащим атомные координаты и скорости.
3. Использовать Snapshot period на 1 шаг данных.
4. Нажать OK, чтобы возвратиться к ячейке диалога Molecular Dynamics Options.
