5 quants / labN2 (O2,HCl)
.docxМИНИСТЕРСТВО ОБРАЗОВАНИЯ И НАУКИ РОССИЙСКОЙ ФЕДЕРАЦИИ
ФЕДЕРАЛЬНОЕ ГОСУДАРСТВЕННОЕ БЮДЖЕТНОЕ ОБРАЗОВАТЕЛЬНОЕ УЧРЕЖДЕНИЕ ВЫСШЕГО ПРОФЕССИОНАЛЬНОГО ОБРАЗОВАНИЯ МИРЭА – РОССИЙСКИЙ ТЕХНОЛОГИЧЕСКИЙ УНИВЕРСИТЕТ
ИНСТИТУТ ТОНКИХ ХИМИЧЕСКИЙ ТЕХНОЛОГИЙ ИМЕНИ М.В. ЛОМОНОСОВА
Кафедра физической химии
им. Сыркина Я.К.
ОТЧЕТ О ЛАБОРАТОРНОЙ РАБОТЕ №2
«Теоретическое изучение электронного и геометрического строения двухатомных молекул методом МО ЛКАО»
Выполнили:
Руководитель работы
Москва, МИТХТ 2018
Цель работы:
1) Расчет основных структурных параметров двухатомных молекул с использованием полуэмпирического метода MNDO.
2) Построение энергетических диаграмм двухатомной гомоядерной и двухатомной гетероядерной молекул по результатам теоретического расчета.
3) Построение и анализ граничных поверхностей молекулярных орбиталей и определение типов симметрии МО.
Объекты: O2, HCl
Расчетный метод: полуэмпирический метод MNDO
Теоретическое введение:















![]()
Результаты расчета:
В лабораторной работе проводился расчет молекулярных характеристик молекул O2 и НСl полуэмпирическим методом MNDO. С помощью программы HyperChem была собрана молекула и скорректирована ее геометрия. Полуэмпирическим методом MNDO был произведен квантово-химический расчет с оптимизацией геометрии.
Из расчета для O2 были найдены:
-
полная энергия E= -14795.126 ккал/моль,
-
межъядерное расстояние rе= 1.14034А0
-
точечная группа симметрии молекулы D∞h
-
энергия ВЗМО= -6.064 (вид симметрии - 1π)
-
энергия НСМО= 6.844 (вид симметрии - 3σg)
-
разность энергий ВЗМО и НСМО: 6.844 -(-6.064)=12.908 эВ
Из расчета для НСl были найдены:
-
полная энергия E= -8514.175 ккал/моль,
-
межъядерное расстояние rе=1.34822А0
-
точечная группа симметрии молекулы С∞v
-
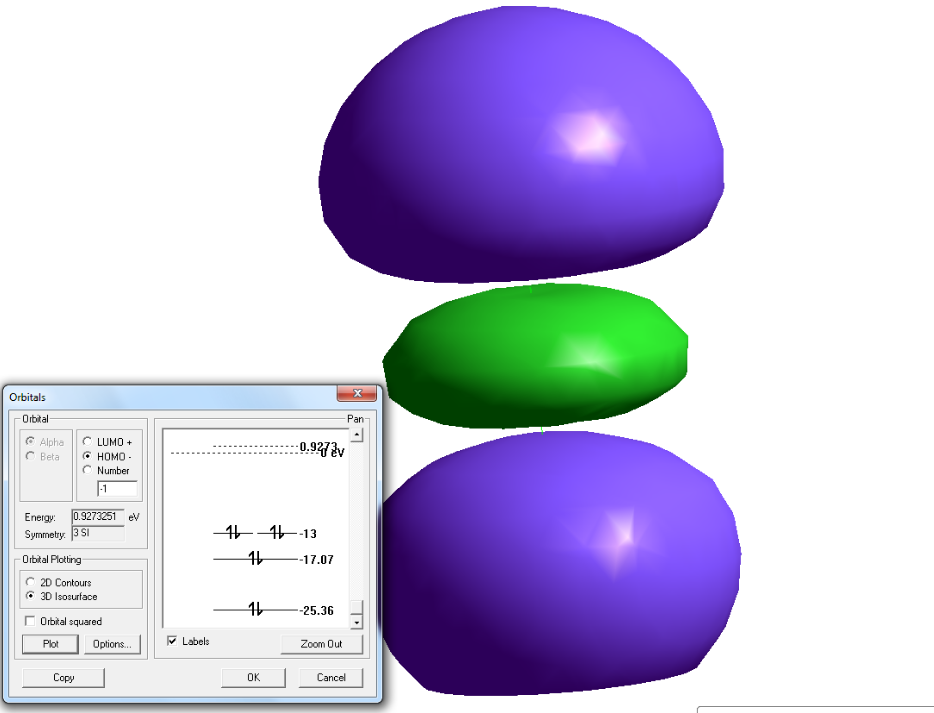
энергия ВЗМО= -13.00122 эВ (вид симметрии - 1π)
-
энергия НСМО= 0.9273251 эВ (вид симметрии - 4σ *)
-
разность энергий ВЗМО и НСМО: 13.9285451 эВ
-
Дипольный момент: рассчитанный μ=1.478 D
HyperChem log start -- Mon Oct 29 16:10:15 2018.
Geometry optimization, SemiEmpirical, molecule = (O2).
MNDO
PolakRibiere optimizer
Convergence limit = 0.0100000 Iteration limit = 50
Accelerate convergence = YES
Optimization algorithm = Polak-Ribiere
Criterion of RMS gradient = 0.0010 kcal/(A mol) Maximum cycles = 30
RHF Calculation:
Triplet state calculation
The half-electron approximation will be used
Number of electrons = 12
Number of Double Occupied Levels = 5
Number of Single Occupied Levels = 2
Charge on the System = 0
Total Orbitals = 8
Starting MNDO calculation with 8 orbitals
E=-134.3720 kcal/mol Grad=0.000 Conv=YES(0 cycles 1 points) [Iter=1 Diff=0.00000]
Eigenvalues (eV) and Eigenvectors
Mol. Orbital 1 2 3 4 5 6
Symmetry: 1 SIG 1 SIU 2 SIG 1 PIU 1 PIU 1 PIG
Eigenvalue -48.70470 -30.04983 -19.21485 -17.47415 -17.47415 -6.06362
S O 1 0.64298 -0.67798 -0.29424 -0.00000 0.00000 -0.00000
Px O 1 -0.00000 -0.00000 -0.00000 -0.67487 -0.21108 -0.63126
Py O 1 0.29424 0.20084 0.64298 -0.00000 -0.00000 -0.00000
Pz O 1 -0.00000 -0.00000 -0.00000 0.21108 -0.67487 0.31862
S O 2 0.64298 0.67798 -0.29424 -0.00000 -0.00000 0.00000
Px O 2 0.00000 -0.00000 0.00000 -0.67487 -0.21108 0.63126
Py O 2 -0.29424 0.20084 -0.64298 -0.00000 -0.00000 0.00000
Pz O 2 0.00000 -0.00000 0.00000 0.21108 -0.67487 -0.31862
Mol. Orbital 7 8
Symmetry: 1 PIG 2 SIU
Eigenvalue -6.06362 6.84370
S O 1 -0.00000 -0.20084
Px O 1 0.31862 0.00000
Py O 1 0.00000 -0.67798
Pz O 1 0.63126 0.00000
S O 2 -0.00000 0.20084
Px O 2 -0.31862 0.00000
Py O 2 -0.00000 -0.67798
Pz O 2 -0.63126 0.00000
ENERGIES AND GRADIENT
Total Energy = -14795.1260118 (kcal/mol)
Total Energy = -23.577531170 (a.u.)
Binding Energy = -134.3719938 (kcal/mol)
Isolated Atomic Energy = -14660.7540180 (kcal/mol)
Electronic Energy = -23347.4540974 (kcal/mol)
Core-Core Interaction = 8552.3280856 (kcal/mol)
HE Energy Correction = -141.6111508 (kcal/mol)
Heat of Formation = -15.2539938 (kcal/mol)
Gradient = 0.0000419 (kcal/mol/Ang)
MOLECULAR POINT GROUP
D*H
EIGENVALUES(eV)
Symmetry: 1 SIG 1 SIU 2 SIG 1 PIU 1 PIU
Eigenvalue: -48.704704 -30.049826 -19.214850 -17.474150 -17.474150
Symmetry: 1 PIG 1 PIG 2 SIU
Eigenvalue: -6.063616 -6.063616 6.843699
ATOMIC ORBITAL ELECTRON POPULATIONS
AO: 1 S O 1 Px O 1 Py O 1 Pz O 2 S O
1.919326 1.500000 1.080674 1.500000 1.919326
AO: 2 Px O 2 Py O 2 Pz O
1.500000 1.080674 1.500000
NET CHARGES AND COORDINATES
Atom Z Charge Coordinates(Angstrom) Mass
x y z
1 8 0.000000 -0.26640 -0.45141 0.00000 15.99900
2 8 -0.000000 -0.26640 0.68893 -0.00000 15.99900
ATOMIC GRADIENTS
Atom Z Gradients(kcal/mol/Angstrom)
x y z
1 8 -0.00000 -0.00007 -0.00000
2 8 0.00000 0.00007 0.00000
Dipole (Debyes) x y z Total
Point-Chg. 0.000 -0.000 0.000 0.000
sp Hybrid -0.000 -0.000 0.000 0.000
pd Hybrid 0.000 0.000 0.000 0.000
Sum -0.000 -0.000 0.000 0.000
HyperChem log stop -- Mon Oct 29 16:10:28 2018.


ВЗМО молекулы O2


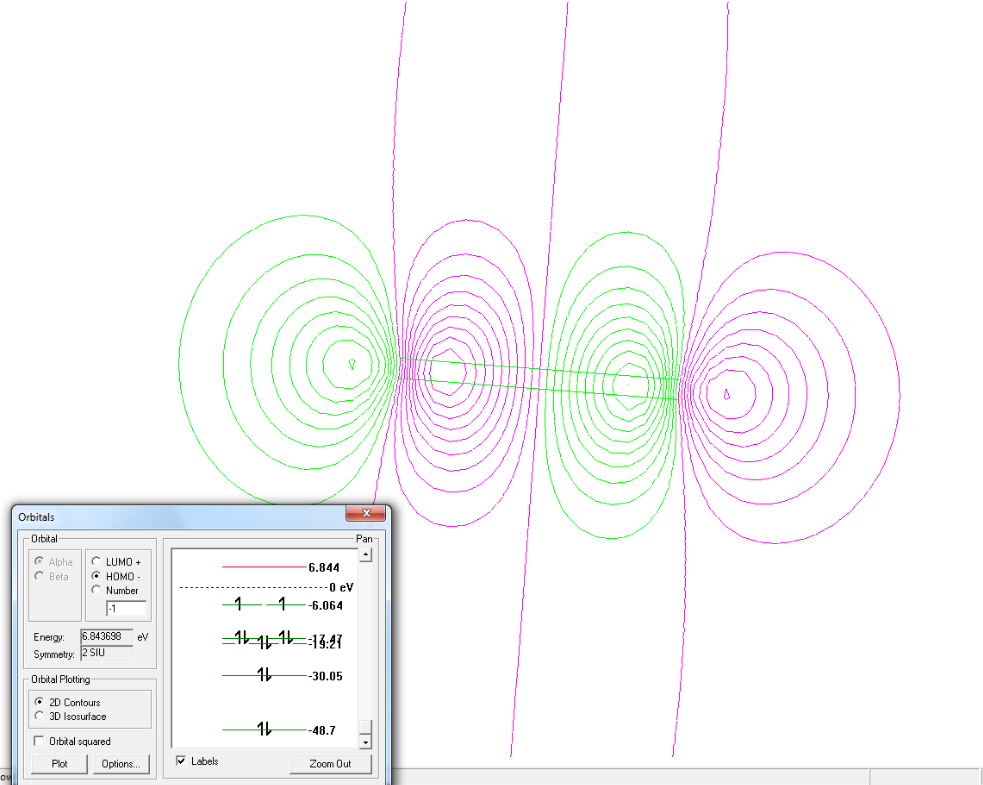
НСМО молекулы О2
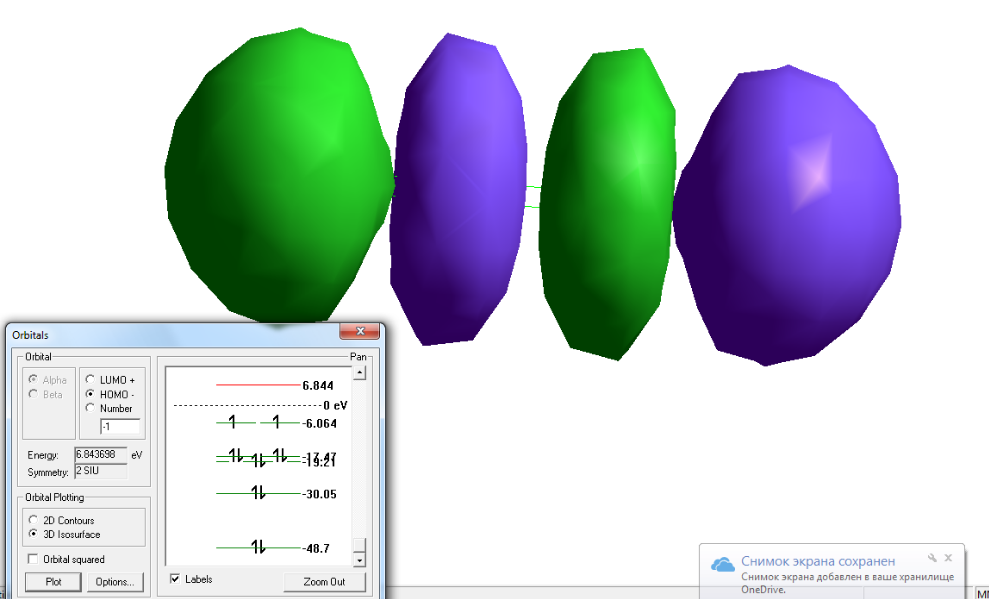

|
|
|
|
|
|
HyperChem log start -- Mon Oct 29 16:58:29 2018.
Geometry optimization, SemiEmpirical, molecule = (HCl).
MNDO
PolakRibiere optimizer
Convergence limit = 0.0100000 Iteration limit = 50
Accelerate convergence = YES
Optimization algorithm = Polak-Ribiere
Criterion of RMS gradient = 0.0010 kcal/(A mol) Maximum cycles = 30
RHF Calculation:
Singlet state calculation
Number of electrons = 8
Number of Double Occupied Levels = 4
Charge on the System = 0
Total Orbitals = 5
Starting MNDO calculation with 5 orbitals
E=-96.3565 kcal/mol Grad=0.000 Conv=YES(2 cycles 11 points) [Iter=1 Diff=0.00000]
Eigenvalues (eV) and Eigenvectors
Mol. Orbital 1 2 3 4 5
Symmetry: 1 SI 2 SI 1 PI 1 PI 3 SI
Eigenvalue -25.36068 -17.07208 -13.00122 -13.00122 0.92732
S Cl 2 0.97089 -0.22131 -0.00000 0.00000 0.09157
Px Cl 2 -0.00000 -0.00000 -0.79230 0.61013 -0.00000
Py Cl 2 -0.11492 -0.76591 0.00000 -0.00000 -0.63259
Pz Cl 2 -0.00000 -0.00000 0.61013 0.79230 -0.00000
S H 1 0.21013 0.60366 0.00000 -0.00000 -0.76905
ENERGIES AND GRADIENT
Total Energy = -8514.1750007 (kcal/mol)
Total Energy = -13.568199845 (a.u.)
Binding Energy = -96.3565367 (kcal/mol)
Isolated Atomic Energy = -8417.8184640 (kcal/mol)
Electronic Energy = -9968.2017011 (kcal/mol)
Core-Core Interaction = 1454.0267004 (kcal/mol)
Heat of Formation = -15.2645367 (kcal/mol)
Gradient = 0.0000022 (kcal/mol/Ang)
MOLECULAR POINT GROUP
C*V
EIGENVALUES(eV)
Symmetry: 1 SI 2 SI 1 PI 1 PI 3 SI
Eigenvalue: -25.360676 -17.072082 -13.001219 -13.001219 0.927323
ATOMIC ORBITAL ELECTRON POPULATIONS
AO: 2 S Cl 2 Px Cl 2 Py Cl 2 Pz Cl 1 S H
1.983229 2.000000 1.199657 2.000000 0.817113
NET CHARGES AND COORDINATES
Atom Z Charge Coordinates(Angstrom) Mass
x y z
2 17 -0.182887 -0.87111 0.00511 0.00000 35.45300
1 1 0.182887 -0.87111 -1.34311 -0.00000 1.00800
ATOMIC GRADIENTS
Atom Z Gradients(kcal/mol/Angstrom)

x y z
2 17 -0.00000 -0.00000 -0.00000
1 1 0.00000 0.00000 0.00000
Dipole (Debyes) x y z Total
Point-Chg. -0.000 -1.184 -0.000 1.184
sp Hybrid -0.000 -0.294 -0.000 0.294
pd Hybrid 0.000 0.000 0.000 0.000
Sum -0.000 -1.478 -0.000 1.478
HyperChem log stop -- Mon Oct 29 16:59:44 2018.


ВЗМО молекулы HCl


НСМО молекулы HCl